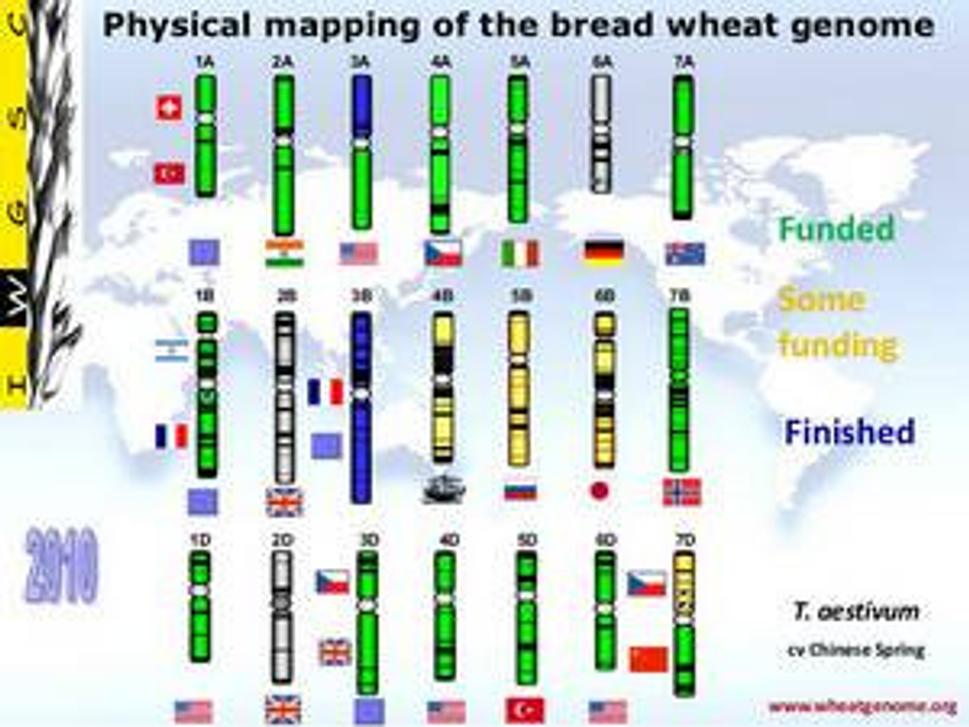
Na hlavnom obrázku tohoto blogu si všimnite akési zelené, modré, žlté a sivé "paličky". Týchto 21 paličiek predstavuje chromozómy pšenice. V predchádzajúcich blogoch sme si hovorili o sekvenciách DNA, takže si možno predstavujete DNA ako nejaký dlhý reťazec písmen. Tých 17 miliárd písmen u pšenice by však bol priveľmi dlhý reťazec. DNA je v bunke ale akoby schúlená do klbôčka - do chromozómu, ktorý vyzerá ako tieto paličky na obrázku. Na tomto obrázku sú paličky, teda chromozómy, zoskupené v troch radoch po siedmych, čo je dohromady 21. V normálnej bunke pšenice je ich však 42 (21 x 2), pretože jedna sada je akokeby od mamy a druhá od otca, presne tak, ako ste už asi počuli, ako to funguje u ľudí. No ale ako vieme, že DNA sa zoskupuje presne do takýchto paličkovitých formácií? V určitej fáze rastu bunky, sú chromozómy tak pekné a tak veľké, že ich môžeme normálne pozorovať pod klasickým mikroskopom.
Pri každnom chromozóme na tomto obrázku si všimnite aj malé vlajočky. To znázorňuje rozdelenie úloh pri sekvenovaní pšenice medzi štáty. Česká vlajka je pri chromozóme 4A, menšej polovici 3D a tiež aj časti 7D. Sekvenovanie pšenice je veľký niekoľkoročný projekt, a preto sa medzinárodné spoločenstvo rozhodlo, že presne rozdelí úlohy medzi štáty, aby sa nestalo, že dve vedecké skupiny budú náhodou pracovať na tom istom.
Ako som už spomínala, chromozómy je možné v určitý moment vidieť pod mikroskopom. A vtedy je dokonca možné ich aj roztriediť. V tomto sú priekopníci vedci z Ústavu experimentální botaniky v Olomouci, ktorí využívajú špeciálny prístroj na triedenie chromozómov (ale aj akýchkoľvek celých buniek), ktorý sa volá cytometer.
Cytometer je senzačný prístroj, ktorý obrovskou rýchlosťou dokáže preskenovať milióny buniek či chromozómov, ktoré doňho vpúšťame v prúde vody. V každej kvapke vody je jedna bunka a tento prístroj dokáže hneď zistiť, akú má táto bunka veľkosť a dokonca či aj vysiela nejaký fluorescenčný svetelný signál. Ak poznáme aspoň kúsok sekvencie chromozómu alebo aj celého genómu, ktorý chceme vyseparovať pomocou cytometra, môžeme ho pomocou takzvanej hybridizácie prinútiť, aby svietil na zeleno či červeno. Hybridizácia je metóda, keď na objekt (bunku, chromozóm), ktorý chceme vyseparovať, naviažeme fluorescenčnú sondu alebo ho nafarbíme flourescenčným farbivom. Tento objekt sa potom v prístroji rozosvieti, prístroj zmeria jeho svetelnú intenzitu a ak je intenzita dostatočne veľká, tak ho vyseparuje do určenej skúmavky. Ako som vám už spomínala v predchádzajúcich blogoch, písmenká sú v dvojreťazcovej DNA kompatibilne naviazané na seba v dvojiciach A-T alebo G-C, teda A v prvom reťazci sa spája s T v druhom reťazci a G sa spája s C a tiež naopak: T sa spája s A a C s G. Fluorescenčná sonda je krátka jednoreťazcová sekvencia DNA, ktorá je kompatibilná k sekvencii v našej bunke / chromozóme a okrem toho má na svojom konci chemickú látku, ktorá dáva svetelný signál. Navrhneme si ju v počítači a necháme si ju vyrobiť u špecializovaných výrobcov DNA na objednávku. Pôsobením rôznych chemických látok a teplôt docielime, že naša flourescenčná sonda sa prilepí na kompatibilný reťazec DNA v našej bunke, ktorú chceme vyseparovať. Prístroj detekuje svetelný signál a bunku naozaj fyzicky uloží do predpripravenej skúmavky. (O cytometri nabudúce napíšem jeden osobitný blog)
Jeden z dôvodov na takéto triedenie chromozómov pšenice je ten, že si štáty rozdelia prácu. Druhý, ale ešte dôležitejší dôvod je ten, že mnohé sekvencie sa v tak veľkom genóme opakujú. Keby sme do sekvenátora hodili celú DNA pšenice len tak bez triedenia na chromozómy, pravdepodobne by sme ju bez predchádzajúcej kostry nikdy v živote nedokázali správne zložiť. V súčasnosti sekvenačné prístroje nedokážu zistiť sekvenciu celej dlhokánskej DNA, ale musíme ju do sekvenátorov vkladať nakrájanú na kúsky, pretože sekvenátor dokáže vyprodukovať len sekvencie cca 500 písmen dlhé. Takže celý genóm pšenice (17 miliárd písmen) by bol nasekaný na 34 000 000 kúskov. Do sekvenátora však ale nedávame len jednu molekulu DNA (tých 17 mld písmen), ale potrebujeme tam dať viac molekúl s tým, že sa každá molekula naseká náhodne na kúsky približne 500 písmen dlhé, čím docielime, že sa kúsky DNA budú prekrývať, a tak ich budeme vedieť lepšie poskladať. Takže by sme tam museli dať niekoľko miliárd kúsočkov dlhých 500 písmen.
V prípade pšenice je to ale veľmi ťažké, pretože mnohé sekvencie sa opakujú na niekoľkých chromozómoch. Keby sme do sekvenátora hodili DNA len tak celú nerozdelenú na chromozómy, mohlo by sa stať, že dostaneme dve veľmi podobné 500 písmenkové sekvencie, nevedeli by sme, či jedna sekvencia je kópia tej druhej alebo či má svoju správnu pozíciu na úplne inom chromozóme.
Sekvenovanie pšenice sa komplikuje ešte viac tým, že sekvencie sa opakujú nielen medzi chromozómami, ale aj v rámci chromozómov. Okrem toho jeden chromozóm má v priemere tak 800 000 000 písmen, čo je stále ešte skoro 200 krát viac než priemerná baktéria. Aj na to vedci našli riešenie. Vezmeme DNA z jedného chromozómu a nakrájame ju na kúsky pomocou strihacích enzýmov (ktoré som vám tu už viackrát spomínala). Strihacie enzýmy pôsobia pozdĺž celej dĺžky DNA, prechádzajú písmenko po písmenku a ak natrafia napríklad na poradie GAATTC, tak prestrihnú DNA presne za písmenkom G. Je niekoľko desiatok rôznych typov týchto strihacích enzýmov a každý z nich má svoju sekvenciu, za ktorou DNA prestrihne. Takto môžeme aj bez predchádzajúcich znalostí sekvencie pšenice, postrihať DNA na kúsky, ktoré budú napríklad len 100 000 písmen dlhé. S takýmito kúskami sa už pracuje oveľa lepšie.
Tieto kúsky DNA sa potom zlepia s takzvaným BAC-om (bacterial artificial chromosome). V predchádzajúcom blogu som vám vysvetľovala klonovanie kúskov DNA do plasmidov. Plasmidy a BAC-y sú v podstate podobné, sú to umelo vyrobené kúsky DNA, ku ktorým lepiacim enzýmom prilepíme náš kúsok DNA. Do BAC-u môžeme na rozdiel od plasmidu vlepiť kúsky aj viac než 100 000 písmen dlhé. Tento zlepenec vo forme kruhu sa potom elektrošokom dostane do baktérie E. coli. Jedna baktéria dostane do seba len jeden kúsoček DNA, každá baktéria teda bude obsahovať iný kúsoček DNA. E.coli je už veľmi dobre známa baktéria a dobre sa kultivuje. Ako E. coli rastie, zároveň nám pomáha namnožiť tento náš kúsok DNA, ktorý v sebe nosí. Takže z jedného kúsku DNA nakoniec získame niekoľko tísíc kópií, a to je už pekné množstvo DNA, ktoré môžeme kľudne vložiť do sekvenátora. Potom môžeme tieto baktérie obshaujúce naše kúsky DNA zmraziť a odložiť na neskoršie použitie a zase niekedy potom rozmnožiť. Takto už náš kúsok DNA nikdy nestratíme.
Takže predstavte si, že máme jeden chromozóm pšenice, ktorý má 800 miliónov písmen. Ten rozstriháme na kúsky 100 000 písmen dlhé, takže dostaneme 8000 kúsočkov, teda 8000 kolónií baktérií, kde každá kolónia bude v sebe nosiť iný kúsok DNA. Vynásobme teraz číslo 8000 počtom chromozómov 21 a vyjde nám, že potrebujeme 168 000 kolónií. A to by sme mali ešte vynásobiť ešte číslom 10 (to číslo môže byť aj vyššie, závisí na dizajne výskumu), pretože strihanie celého genómu potrebujeme zopakovať ešte niekoľkokrát, aby sa nám naše kúsočky prekrývali, a tak budeme vedieť, ako ich poskladať. Teoreticky počítajme 1 680 000 kolónií. Predstavte si, že tieto bakteriálne kolónie vypicháme z kultivačných misiek a usporiadame do dostičiek s 96 jamkami (8 radov x 12 stĺpcov). Takže nakoniec budeme mať zbierku 17 500 dostičiek uložených v mrazáku, ktoré sa budú postupne sekvenovať počas niekoľkých rokov.
Ako som už spomínala, taká priemerná baktéria má genóm dlhý cca 4 000 000 písmen. Jedna BAC kolónia s kúskom DNA pšenice je dlhá 100 000 písmen. To je len 40 krát menej. Jedna baktéria by sa kľudne mohla osekvenovať použitím jednej sekvenačnej dostičky. DNA takejto obyčajnej baktérie by sme tam "len tak frkli" a dokázali by sme ju hneď jednoducho poskladať. My sme v článku Intraspecific sequence comparisons reveal similar rates of non-collinear gene insertion in the B and D genomes of bread wheat skúsili sekvenovať 24 BAC-ov pšenice naraz spolu na jednej sekvenačnej dostičke, čo je podľa teoretického výpočtu ešte menej písmen než jedna primerná baktéria. Ukázalo sa však, že v genóm pšenice je strašne zložitý, pretože sa tam opakuje strašne veľa sekvencií, takže ani týchto 24 BAC-ov nie je také jednoduché sekvenovať dohromady. Chvíľu nám trvalo, kým sme túto skladačku rozlúštili, ale našťastie sa to podarilo.
Potom nasledovalo porovnávanie našich sekvencií s už osekvenovanými genómami ďalších cereálií: ryžou a Brachypodium distachyon. To je veľa práce pri počítači, o čom viac nájdete v mojom minulom blogu. Brachypodium bola prvá osekvenovaná z trávovitých rastlín, pretože má len jednu sadu chromozómov (pšenica má tri). Všimnite si článok v Nature, kde sa oznamuje dokončenie sekvenovania jej genómu. Tam môžete vidieť, že na jej skevenovaní sa podielalo 46 vedeckých skupín z celého sveta. A to má Brachypodium oveľa menší genóm než pšenica.
Možno ste už nedávno čítali, že genóm pšenice sa už osekvenoval, čo nájdete v originále v časopise Nature z novembra 2012. Títo vedci však DNA pšenice do sekvenátora vložili len tak rovno nakrájanú na kúsky dlhé 500 písmen, teda vynechali krok, kde sa majú kúsky dlhé 100 000 písmen vložiť do BAC-ov a až potom separátne nastrihať na 500 písmen. Kedže máme akú-takú ako keby kostru podľa príbuzných druhov, kam by sa mali sekvencie naskladať, dá sa genóm pšenice približne poskladať aj takto rovno bez BAC-ov. Všetky podrobnosti sa však dozvieme až po presnom zložení sekvencií BAC-ov, o ktorom som tu písala, čo zatiaľ ešte hotové na 100% nie je.
Musím ale nakoniec zdôrazniť, že dokončením sekvenovania genómu pšenice alebo akejkoľvek inej rastliny či živočícha nič nekončí, ale práve len začína. Keď sa nájdu nejaké nové gény, musí sa rozlúštiť, načo slúžia a odkiaľ prišli. Popísať funkciu len jedného nového génu, zistiť, aký protein tvorí, čo by sa dalo využiť v šlachtení rastlín... a všetko okolo toho je práca pre celú jednu vedeckú skupinu na niekoľko mesiacov či rokov. Napríklad ryža má už o svojom genóme dokonca vlastný časopis. Takže horsa do práce...






